2016年6月30日,国际著名学术期刊Genome Research在线发表了中国科学院上海生命科学研究院生物化学与细胞生物学研究所陈玲玲研究组和计算生物学研究所杨力研究组关于环形RNA研究的最新进展“Diverse alternative back-splicing and alternative splicing landscape of circular RNAs”。该研究系统绘制了环形RNA可变环化与可变剪接图谱,揭示了环形RNA可以通过可变环化和可变剪接机制产生新的外显子剪接,深入的机制研究表明环形RNA的可变反向剪接受到其上下游内含子互补配对序列的竞争配对调控。
陈玲玲研究组与杨力研究组在2014年首次合作阐明了互补序列对外显子来源环形RNA产生的调控机制,并提出可变环化(alternative circularization)概念,即多个互补序列的选择配对及其动态调控使得一个基因产生多个环形RNA的现象(Cell, 2014, 159: 1488-1489)。
在此项工作中,研究人员利用升级版的CIRCexplorer2开源工具包,进一步深入研究和全面阐述了环形RNA可变环化与可变剪接(alternative splicing)的复杂性和多样性。研究数据表明,环形RNA的可变环化受到其上下游内含子互补配对序列的竞争配对调控,并首体通过生化实验验证此模型;其次,可变剪接不仅发生在线性mRNA水平,在环形RNA中也同样发现了四种已知的通用可变剪接类型,极大地提高了环形RNA的复杂性和多样性。有意思的是,进一步的研究数据显示许多新的外显子特异性地出现在环形RNA中,其数量可高达数百到数千个。研究人员还建立了环形RNA数据库网站(http://www.picb.ac.cn/rnomics/circpedia),对环形RNA在不同样本中的可变环化(和可变剪接)进行全面的注释,以促进环形RNA研究的发展。该工作是研究组对环形RNA新分子探索的最新成果,为系统阐述环形RNA的生成加工及其在体内的潜在生物学功能奠定了坚实的理论基础。
该项研究在陈玲玲研究员和杨力研究员的共同指导下,由计算生物学研究所博士研究生张晓鸥、董瑞和生物化学与细胞生物学研究所的张杨共同完成。该项研究得到了国家基金委、科技部、中科院的经费支持。
文章链接:http://genome.cshlp.org/content/early/2016/06/30/gr.202895.115.long
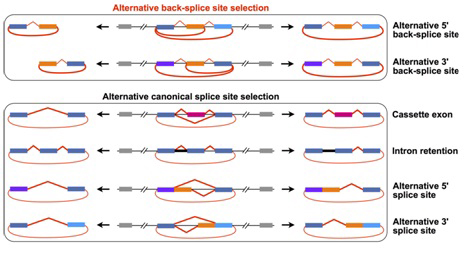
利用升级版的CIRCexplorer2开源工具包全面系统的阐述了环形RNA可变环化(alternative circularization)与可变剪接(alternative splicing)的复杂性和多样性。(图片由陈玲玲研究组提供)